分析内容
标准信息分析
|
1. 原始数据过滤,去除接头序列及低质量reads 2. 数据产出统计及测序质量评估(测序饱和度分析、测序随机性分析) 3. 转录组denovo组装 4. 组装质量统计与分析(Contig N50、Unigene*长度分布、reads覆盖统计) 5. Unigene表达统计(基因覆盖度,表达量、表达量丰度分布) 6. Unigene基本功能注释 6.1 Unigene Nr蛋白数据库注释 6.2 Unigene SwissProt蛋白数据库注释 6.3 Unigene COG/KOG注释及分类 6.4 Unigene GO功能注释及分类 6.5 Unigene Pathway代谢通路注释 7. Unigene高级功能注释 7.1 预测编码蛋白框(CDS)及Unigene序列方向预测 *此处Unigene 等同于“转录本”或“Transcript” 7.2 近缘模式生物同源基因CDS比较 7.3 Pfam蛋白结构域分析 |
8. SSR开发及引物设计 9. 样本关系分析(主成分分析(PCA)、相关性系数热图、样本聚类图) 10. 差异表达基因分析(两个或两个以上样品) 10.1 差异表达基因筛选
10.2 差异基因火山图
10.3 差异基因表达模式聚类分析(热图)
10.4 差异基因GO功能显著性富集分析
10.5 差异基因Pathway显著性富集分析
11 互作网络分析 12 GSEA分析 13 突变分析(SNP/InDel分析) 14 omicmart 在线报告
|
高级信息分析
研究思路
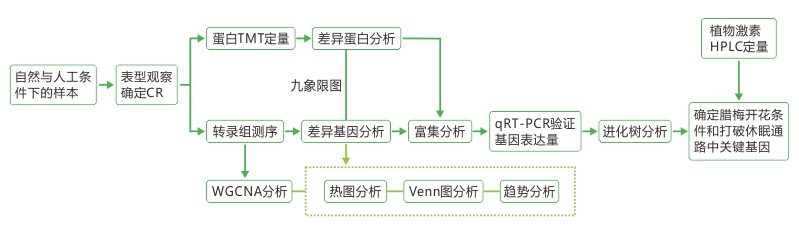
研究结果
|
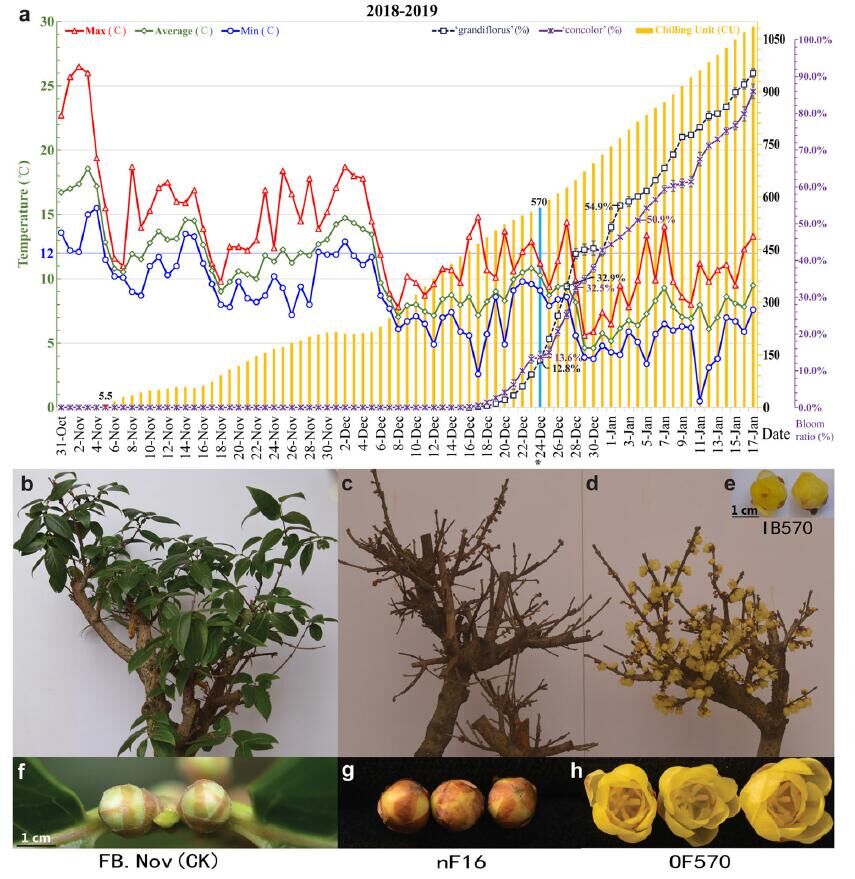
表型观察确定CR 作者监测了在不同CU下开花率的情况,结合自然和人工条件发现在短日照(SDs,8/16h,12℃)低温(LT)自然条件下,CR达到570CU,蜡梅花芽会打破冬眠开花。
转录组测序结果
罗列转录组测序结果,包括contigs数量、N50的值、转录本平均长度、利用NR、Swissprot、KOG和KEGG数据库注释到的unigenes数量。
①差异分析
②WGCNA |
图1 自然和人工条件下的测定CR和表型图片,OF570为IB570开花后的状态 |
|
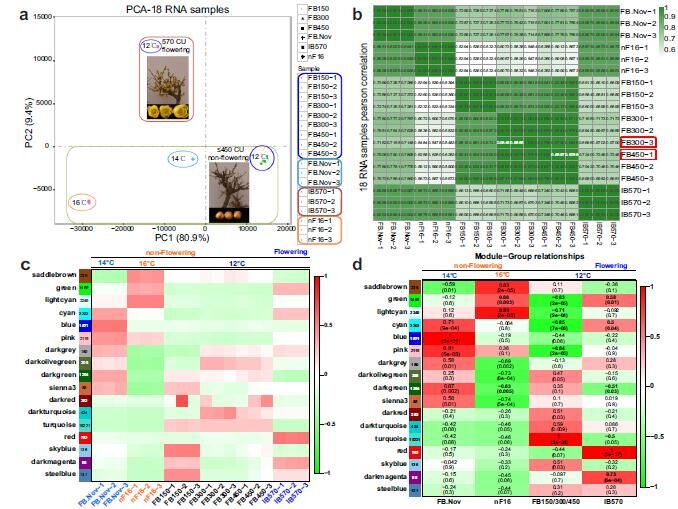
图2 PCA、Pearson相关性分析、WGCNA分析结果 |
Hub genes是模块中连通其他基因数量最多的基因,kME是每个基因在每个模块中的表示连通性大小的值,P值是对应的显著性。作者用kME > 0.95,P < 10e−8作为核心基因(hub gene)的筛选条件,共筛选出7.042个hub genes。对其中76个DEGs用Cytoscape构建网络图。
|
|
③韦恩图分析、趋势分析、热图分析 |
图3 韦恩图分析、趋势分析、热图分析结果
|
转录与蛋白组学关联分析
|
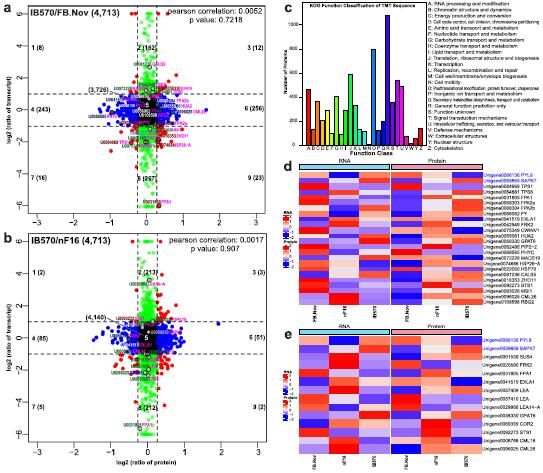
图4 九象限图相关分析,TMT定量蛋白功能分析,RNA和蛋白热图分析 |
为进一步找到和打破休眠相关的关键基因,联合蛋白质组学数据进行分析。
结果发现在IB570/FB.Nov中大部分都是蛋白发生表达,而mRNA没有变化,说明IB570大部分蛋白的增加与转录或翻译过程无关,IB570/nF16中大部分蛋白发生下调,对其中24,14个unigenes和蛋白绘制了组合热图。 |
|
DEGs验证和进化树分析
|
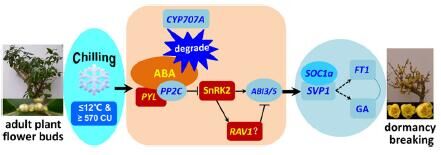
图5 文章推测的低温诱导的蜡梅休眠打破通路 |